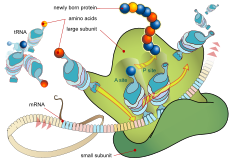
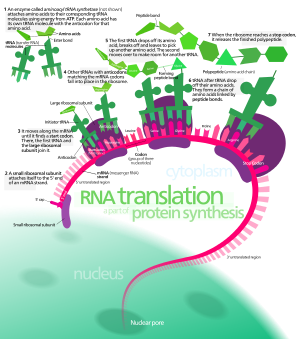
Translacja (tłumaczenie) jest drugim etapem biosyntezy białek i częścią procesu ekspresji genów. W trakcie translacji informacja zawarta w sekwencji nukleotydów mRNA jest odczytywana w celu zbudowania łańcucha polipeptydowego — przyszłego białka.
Zanim rozpocznie się translacja, zachodzą etapy przetwarzania informacji genetycznej:
- transkrypcja — proces, w którym z DNA powstaje pre-mRNA zawierające zarówno eksony, jak i introny;
- Łączenie RNA za pomocą splicosomów — czyli wycinanie intronów i składanie eksonów, co prowadzi do powstania dojrzałego mRNA;
- transport do cytoplazmy i sformułowanie posłańca RNA (mRNA) gotowego do translacji — u eukariontów mRNA jest dodatkowo modyfikowane (5' cap, poliadenylacja), a następnie eksportowane z jądra.
U eukariontów tłumaczenie odbywa się na rybosomach w cytoplazmie oraz na rybosomach związanych z siatką endoplazmatyczną (RE). U bakterii tłumaczenie odbywa się w cytoplazmie, ponieważ brak im jądra i procesy transkrypcji i translacji mogą zachodzić jednocześnie (są sprzężone).
Rola mRNA
mRNA (ang. messenger RNA) przenosi informację o kolejności aminokwasów zakodowaną w DNA. Informacja jest odczytywana w trójkowych jednostkach — kodonach (po trzy nukleotydy). Jeden kodon odpowiada jednemu aminokwasowi (z wyjątkiem kodonów STOP, które sygnalizują zakończenie translacji). Sekwencja startowa (najczęściej AUG kodujący metioninę) determinuje miejsce rozpoczęcia odczytu i ramkę odczytu.
Budowa rybosomu i jego rola
Rybosomy składają się z małej i dużej podjednostki. Mała podjednostka wiąże mRNA i umożliwia odczytanie kodonów, a duża podjednostka katalizuje tworzenie wiązań peptydowych między aminokwasami (aktywność peptydylotransferazowa jest właściwością rRNA). Rybosom ma miejsca A (aminoacylowe), P (peptydylowe) i E (exit) — miejsca te uczestniczą w cyklu wprowadzania na miejsce następnego tRNA, tworzenia więzania peptydowego i uwalniania pustego tRNA.
tRNA i ładowanie aminokwasów
Aminokwasy są przenoszone do rybosomu przez specyficzne cząsteczki tRNA, które mają region antykodonu komplementarny do kodonu mRNA. Każdy tRNA posiada konkretny antykodon i jest naładowany odpowiednim aminokwasem przez enzymy aminoacyl-tRNA syntetazy. To enzymy te rozpoznają zarówno aminokwas, jak i odpowiedni tRNA, więc to one gwarantują poprawne sparowanie antykodon–aminokwas.
Mechanizm translacji — etapy
Inicjacja: Mała podjednostka rybosomu oraz inicjacyjne tRNA (niosące metioninę) wiążą się z mRNA przy odpowiednim miejscu startowym (u prokariotów często za pomocą sekwencji Shine-Dalgarno, u eukariontów rozpoznawana jest struktura 5' cap i kontekst Kozaka). Następnie dołącza duża podjednostka, tworząc funkcjonalny rybosom gotowy do elongacji.
Elongacja: Do miejsca A wchodzi aminoacylowane tRNA komplementarne do aktualnego kodonu mRNA. W miejscu P znajduje się łańcuch peptydowy związany z poprzednim tRNA. Enzymatyczna część dużej podjednostki katalizuje przeniesienie łańcucha peptydowego z tRNA w miejscu P na aminokwas przyłączony do tRNA w miejscu A (tworzenie wiązania peptydowego). Rybosom przesuwa się o jeden kodon, przenosząc tRNA z P do E (uwolnienie) i z A do P, a miejsce A zostaje wolne dla następnego aminoacyl-tRNA.
Terminacja: Gdy w miejscu A pojawi się kodon STOP (UAA, UAG, UGA), nie istnieje odpowiadający mu tRNA. Zamiast tego działają czynniki uwalniające (release factors), które inicjują hydrolizę wiązania między łańcuchem polipeptydowym a tRNA w miejscu P, prowadząc do uwolnienia nowo powstałego polipeptydu i dysocjacji kompleksu translacyjnego.
Dalsze losy polipeptydu — fałdowanie i modyfikacje
Powstały łańcuch polipeptydowy często wymaga fałdowania (często z pomocą białek opiekuńczych — chaperonów) oraz modyfikacji potranslacyjnych — np. odcinania peptydów sygnałowych, glikozylacji, fosforylacji, tworzenia mostków disiarczkowych. Te modyfikacje wpływają na funkcję, trwałość i lokalizację białka.
Kierowanie białek do siateczki endoplazmatycznej i dalszy transport
Wiele rybosomów wraz z mRNA przyczepia się do zewnętrznej błony siateczki endoplazmatycznej. Białka przeznaczone do eksportu, wbudowania w błony lub do lizosomów zawierają sekwencję sygnałową rozpoznawaną przez cząsteczkę SRP (signal recognition particle), co zatrzymuje translację i kieruje rybosom do receptora w błonie RE. Nowo syntezowane białka trafiają do wnętrza siateczki endoplazmatycznej, skąd są pakowane do pęcherzyków i transportowane do innych organelli lub wydzielane na zewnątrz komórki.
Różnice między prokariotami a eukariotami
Główne różnice obejmują m.in.:
- u prokariotów transkrypcja i translacja mogą być sprzężone czasowo i przestrzennie (brak jądra);
- mechanizmy inicjacji różnią się — sekwencja Shine-Dalgarno u bakterii vs 5' cap i kontekst Kozaka u eukariontów;
- u eukariontów mRNA jest zwykle modyfikowane (5' cap, poli-A) i eksportowane z jądra przed translacją;
- skład rybosomów i niektóre białka czynników translacyjnych różnią się między typami komórek.
Inne istotne cechy
Kod genetyczny jest zdegenerowany — wiele kodonów może kodować ten sam aminokwas. Również błędy translacyjne występują rzadko dzięki specyficzności parowania antykodon–kodon oraz dokładności działania aminoacyl-tRNA syntetaz. Rybosomy i rRNA odgrywają centralną rolę w dokładności i szybkości syntezy białek.
Podsumowując, translacja to złożony, ściśle kontrolowany proces przekształcania informacji genetycznej zawartej w mRNA w funkcjonalne białka, wymagający współpracy mRNA, rybosomów, tRNA, enzymów i licznymi mechanizmami kontrolnymi zapewniającymi poprawność i właściwe przeznaczenie syntezowanych białek.